Introducción a DeepXDE: Resolver la ecuación de Poisson 1D#
Autor: José Robledo
Introducción#
En esta notebook vamos a usar una Physics-Informed Neural Network (PINN) para resolver una ecuación diferencial con DeepXDE. La idea es convertir un problema clásico de ecuaciones diferenciales en un problema de aprendizaje: en vez de aproximar datos, entrenamos una red para que respete una ley física.
El problema que queremos resolver es la ecuación de Poisson 1D:
con \(x\in[-1,1]\) y condiciones de contorno de Dirichlet
En este caso conocemos la solución exacta:
Eso convierte este ejemplo en una muy buena puerta de entrada a DeepXDE, porque podemos comparar la predicción de la PINN contra la solución analítica y entender qué está aprendiendo la red en cada etapa.
DeepXDE#
DeepXDE es una librería de código abierto diseñada para resolver ecuaciones diferenciales utilizando redes neuronales informadas por física (PINNs) y otros métodos basados en aprendizaje automático. Permite formular problemas directos e inversos combinando datos y leyes físicas (expresadas como ecuaciones diferenciales) en una misma función de pérdida, evitando la necesidad de mallas tradicionales como en métodos numéricos clásicos. Soporta múltiples backends (TensorFlow, PyTorch, JAX) y ofrece herramientas para definir geometrías, condiciones de contorno e iniciales, así como para entrenar modelos de forma eficiente. Por su flexibilidad, es especialmente útil en problemas donde los datos son escasos pero la física es conocida, como en difusión, elasticidad o ecuaciones de Helmholtz.
El flujo típico de DeepXDE consiste en:
escribir el residuo de la ecuación,
definir la geometría del dominio,
imponer las condiciones de contorno (CC),
armar el objeto
dde.data.PDE, donde se combina la geometría, la PDE, las CC, y los puntos de colocación.definir la red neuronal,
entrenar el modelo.
!pip install -q deepxde
[notice] A new release of pip is available: 26.0.1 -> 26.1
[notice] To update, run: pip install --upgrade pip
1. Escribir la física del problema#
En DeepXDE, la ecuación diferencial se expresa como una función de Python que devuelve el residuo de la PDE. Si la red aprendiera exactamente la solución, ese residuo debería valer cero en todo el dominio.
Crearemos una función llamada pde(x, y) que recibe:
x: los puntos del dominio,y: la salida actual de la red evaluada en esos puntos.
import os
# necesario para obligar a deepxde a usar el framework de pytorch.
os.environ['DDE_BACKEND'] = "pytorch"
import deepxde as dde
import torch
import numpy as np
torch.set_default_device("cpu")
def pde(x, y):
dy_xx = dde.grad.hessian(y, x)
return dy_xx + torch.pi**2 * torch.sin(torch.pi * x)
def sol_exacta(x):
# yo forcé a utilizar torch, pero DeepXDE está diseñado para trabajar con numpy, así que también se podría usar numpy aquí
if isinstance(x, np.ndarray):
x = torch.tensor(x, dtype=torch.float32)
return torch.sin(torch.pi * x).cpu()
Using backend: pytorch
Other supported backends: tensorflow.compat.v1, tensorflow, jax, paddle.
paddle supports more examples now and is recommended.
dde.grad.hessian?
Usamos autodiferenciación para calcular \(d^2y/dx^2\) con dde.grad.hessian (existe también dde.grad.gradients y dde.grad.jacobian) y definimos la solución exacta para comparar el resultado del entrenamiento.
dir(dde.grad)
['__all__',
'__builtins__',
'__cached__',
'__doc__',
'__file__',
'__loader__',
'__name__',
'__package__',
'__path__',
'__spec__',
'clear',
'gradients',
'gradients_forward',
'gradients_reverse',
'hessian',
'jacobian']
2. Definir la geometría del dominio#
La geometría le dice a DeepXDE dónde vive el problema. Como estamos en una dimensión y el dominio es \([-1,1]\), usamos dde.geometry.Interval.
Este objeto no solo representa el intervalo: también será la base para generar puntos interiores, reconocer el borde y construir el problema completo.
geom = dde.geometry.Interval(-1, 1)
Otras geometrías posibles y utiles son
dde.geometry.Rectangle([x_min, y_min], [x_max, y_max]) # plano 2D rectangular
dde.geometry.TimeDomain(t0, t1) # dominio de tiempo
dde.geometry.GeometryXTime(geom, timedomain) # dominio espacio y tiempo
dde.geometry.Cuboid([x_min, y_min, z_min], [x_max, y_max, z_max]) # cubo
dde.geometry.Hypercube(...) # hibercubo
dde.geometry.Disk(center, radius) # disco
dde.geometry.Sphere(center, radius) # esfera
dde.geometry.Polygon(vertices) # poligono
dir(dde.geometry)
['CSGDifference',
'CSGIntersection',
'CSGUnion',
'Cuboid',
'Disk',
'Ellipse',
'Geometry',
'GeometryXTime',
'Hypercube',
'Hypersphere',
'Interval',
'PointCloud',
'Polygon',
'Rectangle',
'Sphere',
'StarShaped',
'TimeDomain',
'Triangle',
'__all__',
'__builtins__',
'__cached__',
'__doc__',
'__file__',
'__loader__',
'__name__',
'__package__',
'__path__',
'__spec__',
'csg',
'geometry',
'geometry_1d',
'geometry_2d',
'geometry_3d',
'geometry_nd',
'pointcloud',
'sample',
'sampler',
'timedomain']
3. Pensar los datos y los puntos de colocación#
En una PINN, la ecuación se fuerza sobre un conjunto de puntos del dominio llamados collocation points o puntos de colocación. Hay varias maneras de de incluirlos. Es en estos puntos donde se debe cumplir la pérdida física. Para esto vamos a utilizar num_domain o anchors más adelante en la definición de PDE. num_domain=16 muestreará de manera aleatoria 16 puntos dentro del dominio definido, mientras que anchors permitirá definir los puntos específicos donde se debe cumplir.
A continuación se generan 10 puntos en el intervalo [−1,0] y se calcula la solución exacta en esos puntos (esto sería los datos observados). Luego, esos pares (x,u) se usan para agregar una pérdida de datos (tipo MSE) que obliga a la red a coincidir con esos valores durante el entrenamiento.
x_train = np.linspace(-1, 0, 10).reshape(-1, 1)
y_train = sol_exacta(x_train).cpu()
observe_u = dde.icbc.PointSetBC(x_train, y_train, component=0)
Una alternativa a datos equiespaciados que es muy utilizada es la de muestrear de manera hipercubo latino con LatinHypercube de scipy
from scipy.stats import qmc
sampler = qmc.LatinHypercube(d=1)
x = sampler.random(n=100)
x_train = torch.tensor(2 * x - 1, dtype=torch.float32)
4. Imponer condiciones de contorno#
Ahora codificamos la información física en el borde del dominio. En este problema necesitamos imponer
En DeepXDE, una condición de Dirichlet se construye con dde.DirichletBC. Para eso definimos:
una función que detecta si un punto está en el contorno,
una función que devuelve el valor que queremos imponer sobre ese contorno.
Aunque acá también escribimos explícitamente x_bc e y_bc, el objeto bc es la pieza clave que después usa DeepXDE durante el entrenamiento.
x_bc = torch.tensor([[-1.0], [1.0]], dtype=torch.float32).cpu()
y_bc = torch.tensor([[0.0], [0.0]], dtype=torch.float32).cpu()
# auxiliar para los puntos en el contorno
def contorno(x, en_contorno):
return en_contorno
# función auxiliar para los valores en el contorno
def func_contorno(x):
return 0
# definición de las condiciones de contorno del problema de dirichlet
bc = dde.DirichletBC(geom, func_contorno, contorno)
En principio, la función de contorno puede ser más compleja, por ejemplo si quisieramos sólo restringir la condición al contorno izquierdo, podríamos escribir
def borde_izq(x, on_boundary):
return on_boundary and np.isclose(x[0], -1)
o si quisiesemos solo el borde derecho
def borde_izq(x, on_boundary):
return on_boundary and np.isclose(x[0], 1)
5. Armar el problema para DeepXDE#
El objeto dde.data.PDE junta en un solo lugar todo lo necesario para entrenar:
la geometría,
la ecuación diferencial,
las condiciones de contorno,
cuántos puntos interiores y de borde usar.
En este ejemplo usaremos los 10 datos observados, 16 puntos de colocación, y 2 puntos de contorno. Además pasamos solution=sol_exacta, que es opcional, para que DeepXDE pueda reportar una métrica contra la solución analítica.
data = dde.data.PDE(geometry=geom,
pde=pde,
bcs=[observe_u, bc],
num_domain=16, # puntos para entrenar, puntos de colocación internos
num_boundary=2,
solution=sol_exacta,
num_test=100 # puntos para evaluar, calcular métricas
)
6. Elegir la red neuronal#
Una PINN sigue siendo una red neuronal estándar, pero entrenada con una función de pérdida informada por física. Acá usamos una red totalmente conectada (FNN) con:
1 entrada: la coordenada \(x\),
3 capas ocultas de 50 neuronas,
1 salida: la aproximación de \(y(x)\).
La activación tanh suele funcionar bien en PINNs porque es suave y facilita el cálculo de derivadas. La inicialización Glorot normal ayuda a arrancar el entrenamiento en una escala razonable.
# una entrada, una salida, y 3 capas ocultas de 50 neuronas cada una
capas = [1] + [50]*3 + [1]
# Función de activación tangente hiperbólica
activacion = "tanh"
# Inicialización de los pesos con la distribución Glorot normal
inicializacion = "Glorot normal"
# definición de la red neuronal
red = dde.nn.FNN(capas, activacion, inicializacion)
7. Compilar y entrenar el modelo#
Acá aparecen dos objetos centrales de DeepXDE:
dde.Model(data, red): combina el problema físico con la red,compile(...): define el optimizador y las métricas.
Durante el entrenamiento, la pérdida mezcla el error en el residuo de la ecuación y el error en las condiciones de contorno. Si todo va bien, ambos deberían bajar.
modelo = dde.Model(data, red)
modelo.compile("adam", lr=0.001, metrics=["l2 relative error"])
loss_hist, train_state = modelo.train(epochs=4000)
Compiling model...
'compile' took 1.000647 s
Warning: epochs is deprecated and will be removed in a future version. Use iterations instead.
Training model...
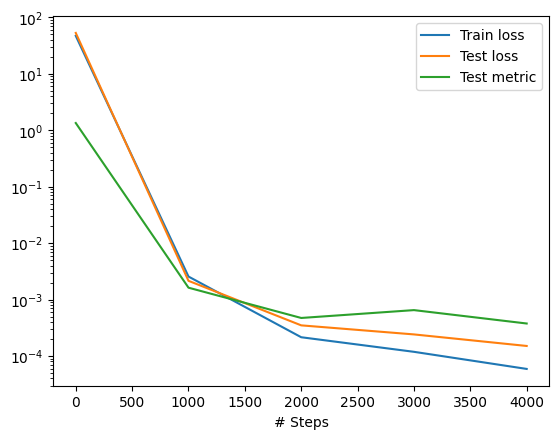
Step Train loss Test loss Test metric
0 [4.58e+01, 8.11e-01, 2.08e-01] [5.17e+01, 8.11e-01, 2.08e-01] [1.34e+00]
1000 [2.55e-03, 4.66e-07, 3.32e-06] [2.14e-03, 4.66e-07, 3.32e-06] [1.62e-03]
2000 [2.15e-04, 1.92e-07, 1.15e-07] [3.49e-04, 1.92e-07, 1.15e-07] [4.72e-04]
3000 [1.18e-04, 3.45e-07, 3.69e-07] [2.41e-04, 3.45e-07, 3.69e-07] [6.50e-04]
4000 [5.88e-05, 8.23e-08, 1.89e-07] [1.50e-04, 8.23e-08, 1.89e-07] [3.77e-04]
Best model at step 4000:
train loss: 5.91e-05
test loss: 1.51e-04
test metric: [3.77e-04]
'train' took 9.703638 s
Como definimos una condición de contorno más la condición física, se imprimen tres funciones de costo.
Step Train loss Test loss Test metric
0 [4.28e+01, 4.20e-01, 1.81e-03] [4.84e+01, 4.20e-01, 1.81e-03] [9.65e-01]
4.28e+01 corresponde a la pérdida MSE (siempre primer elemento) con respecto a los datos
4.20e-01 corresponde a la pérdida física en los puntos de colocación.
1.81e-03 corresponde a la pérdida con condición de contorno bc. que le pasamos a PDE(bcs=bc).
Como agregamos un conjunto de datos de prueba y pasamos metrics=["l2 relative error"] a model.compile, imprime la métrica de prueba Test metric=9.65e-01.
Podemos graficar rápidamente utilizando la funcionalidad del paquete:
dde.saveplot(loss_hist, train_state, issave=False, isplot=True)
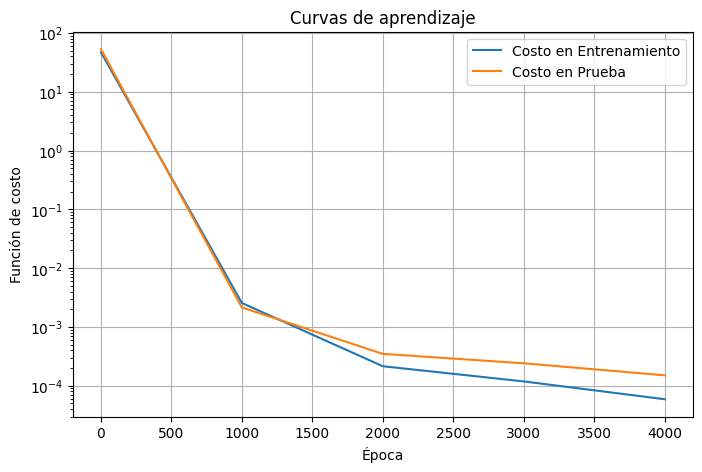
Podemos extraer los datos y hacer nuestras figuras propias
import matplotlib.pyplot as plt
import numpy as np
train_loss = np.array(loss_hist.loss_train)
test_loss = np.array(loss_hist.loss_test)
steps = np.array(loss_hist.steps)
plt.figure(figsize=(8,5))
plt.plot(steps, train_loss.sum(axis=1), label="Costo en Entrenamiento")
plt.plot(steps, test_loss.sum(axis=1), label="Costo en Prueba")
plt.yscale("log")
plt.xlabel("Época")
plt.ylabel("Función de costo")
plt.title("Curvas de aprendizaje")
plt.legend()
plt.grid(True)
plt.show()
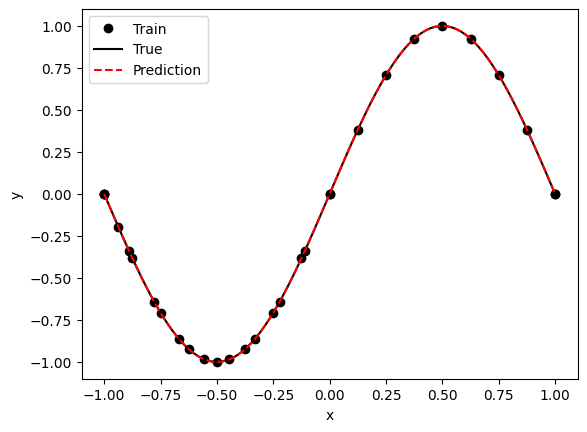
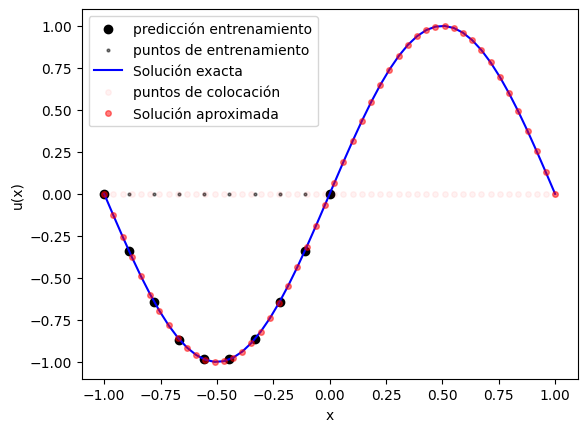
8. Comparar dentro del dominio de entrenamiento#
Primero evaluamos la PINN en puntos del intervalo \([-1,1]\), que es donde realmente está definido el problema.
Acá conviene mirar:
si la curva azul sigue la forma sinusoidal,
si respeta los valores en el borde,
si la diferencia visual con la solución exacta parece pequeña.
x = geom.uniform_points(50, True)
X_domain = data.train_x[:data.num_domain]
y_pred_train = modelo.predict(x_train)
y_exact_train = sol_exacta(x_train)
y_pred = modelo.predict(x)
y_exact = sol_exacta(x).cpu()
import matplotlib.pyplot as plt
plt.figure()
plt.scatter(x_train, y_pred_train, color='black', label="predicción entrenamiento")
plt.scatter(x_train, np.zeros_like(x_train), color='black', label="puntos de entrenamiento", alpha=0.5, s=4)
plt.plot(x, y_exact, 'b', label="Solución exacta")
plt.plot(x, np.zeros_like(x), 'or', label="puntos de colocación", alpha=0.05, ms=4)
plt.plot(x, y_pred, 'or', label="Solución aproximada", alpha=0.5, ms=4)
plt.xlabel("x")
plt.ylabel("u(x)")
plt.legend()
plt.show()
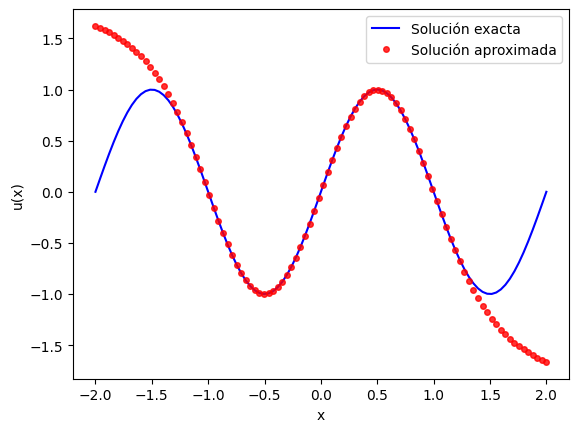
9. Qué pasa fuera del dominio#
En la siguiente celda extrapolamos la solución a \([-2,2]\). Esto es interesante porque muestra una lección práctica importante: una PINN aprende bien donde fue entrenada y donde se impuso la física, pero no necesariamente fuera de ese dominio.
Pregunta para pensar: si el modelo se desvía fuera de \([-1,1]\), ¿eso significa que entrenó mal, o simplemente que nunca le pedimos respetar la ecuación allí?
x = torch.linspace(-2,2,100).reshape(-1,1).cpu()
y_pred = modelo.predict(x)
y_exact = sol_exacta(x).cpu()
import matplotlib.pyplot as plt
plt.figure()
plt.plot(x, y_exact, 'b', label="Solución exacta")
plt.plot(x, y_pred, 'or', label="Solución aproximada", alpha=0.8, ms=4)
plt.xlabel("x")
plt.ylabel("u(x)")
plt.legend()
plt.show()